Pseudočvor
Pseudočvor je sekundarna struktura nukleinskih kiselina koja se sastoji od bar dve strukture matičnih petlji pri čemu je polovina jedne petlje interkalirana između polovina druge. Pseudočvor je inicijalno prepoznat u žutom mozaičnom virusu repe 1982.[2] Pseudočvorovi se savijaju u trodimenzionalne konformacije s oblikom čvora, mada oni nisu pravi topološki čvorovi.
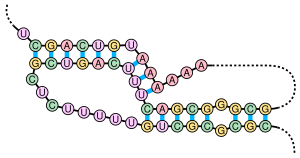

Predviđanje i identifikacija uredi
Strukturna konfiguracija pseudočvorova nije podesna za bioračunarsku detekciju zbog svoje kontekstne senzitivnosti ili “preklapajuće” prirode. Uparivanje baza u pseudočvorovima je nepotpuno; drugim rečima, postoje bazni parovi koji se međusobno preklapaju u sekventnoj poziciji. To otežava predviđanje prisustva pseudočvorova u RNK sekvencama putem standardnih metoda dinamičkim programiranjem, koji koriste rekurzivnu sistem vrednovanja pri identifikaciji uparenih lanaca i konsekventno, većina njih ne može da detektuje bazne parove koji nisu ugneždeni. Noviji metod stohastičke bezkontekstne gramatike ima isti problem. Stoga, popularni metodi za predviđanje sekundarne strujture kao što su Mfold[3] i Pfold[4] ne nalaze strukture pseudočvora prisutne u upitnoj sekvenci; oni jedino identifikuju stabilniju od dve pseudočvorne petlje.
Moguće je identifikovati ograničenu klasu pseudočvorova koristeći dinamičko programiranje, mada ti metodi nisu iscrpni i manje su primenljivi na duže sekvence od nepseudočvorovnih algoritama.[5][6] Opšti problem predviđanja pseudočvorne strukture sa najnižom slobodnom energijom je NP-kompletno.[7][8]
Biološki značaj uredi
Nekoliko važnih bioloških procesa je zavisno od RNK molekula koji formiraju pseudočvorove, koji obično imaju ektenzivnu tercijarnu strukturu. Na primer, pseudočvorni region RNaze P je jedan od najviše konzerviranih elemenata tokom evolucije. RNK komponenta telomeraze sadrži pseudočvor koji je kritičan za aktivnost,[1] i nekoliko virusa koristi strukturu pseudočvora za formiranje motiva sličnog tRNK za infiltraciju ćelija domaćina.[9]
Reference uredi
- ↑ 1,0 1,1 Chen JL, Greider CW. (2005). "Functional analysis of the pseudoknot structure in human telomerase RNA". Proc Natl Acad Sci USA 102(23): 8080–5.
- ↑ Staple DW, Butcher SE (June 2005). „Pseudoknots: RNA structures with diverse functions”. PLoS Biol. 3 (6): e213. DOI:10.1371/journal.pbio.0030213. PMC 1149493. PMID 15941360. Pristupljeno 2010-07-15.
- ↑ „Mfold”. Arhivirano iz originala na datum 2006-04-26. Pristupljeno 2014-06-27.
- ↑ „Pfold”. Arhivirano iz originala na datum 2012-05-10. Pristupljeno 2014-06-27.
- ↑ Rivas E, Eddy S. (1999). "A dynamic programming algorithm for RNA structure prediction including pseudoknots". J Mol Biol 285(5): 2053–2068.
- ↑ Dirks, R.M. Pierce N.A. (2004) An algorithm for computing nucleic acid base-pairing probabilities including pseudoknots. "J Computation Chemistry". 25:1295-1304, 2004.
- ↑ Lyngsø RB, Pedersen CN. (2000). "RNA pseudoknot prediction in energy-based models". J Comput Biol 7(3–4): 409–427.
- ↑ Lyngsø, R. B. (2004). Complexity of pseudoknot prediction in simple models. Paper presented at the ICALP.
- ↑ Pleij CW, Rietveld K, Bosch L (1985). „A new principle of RNA folding based on pseudoknotting.”. Nucleic Acids Res 13 (5): 1717–31. DOI:10.1093/nar/13.5.1717. PMC 341107. PMID 4000943.
Vanjske veze uredi
- Rfam entry for Pseudoknots Arhivirano 2013-12-03 na Archive.is-u